160種類のタンパク質における180種類のホットスポットを同定
出典
- "Systematic characterization of pan‐cancer mutation clusters" Buljan M, Blattmann P, Aebersold R, Boutros M. Mol Syst Biol. 2018 Mar 23;14(3):e7974
- [crisp_bio注]2018年4月に米国のTCGA プロジェクト10年の成果が"Pan-Cancer Atlas"として26編の論文に結実したが、ETH ZurichとDKFZの研究チームによる本論文はそれに先立つ2018年3月23日刊行
背景
- NGS技術の進歩と普及により、癌細胞の多様な遺伝変異および低頻度ロングテールの遺伝変異が大量に報告されるに至った。このため、癌の研究において、ドライバーかパッセンジャーかなど癌化に及ぼす遺伝変異の作用を腑分けすることや、癌細胞における高頻度な遺伝変異が細胞過程に与える作用の解明が、重要な課題になっている。
- 細胞過程はタンパク質とその相互作用により直接的に調節されるが、大規模な癌ゲノム解析イニシアティブであるTCGAとICGCにおいても、遺伝変異がどのようにタンパク質の特性に影響を与えるかについては十分な解析が行われていなかった。
- ETH ZurichとDKFZの研究チームは今回、DNA変異をタンパク質配列にマッピングし、タンパク質配列上で変異頻度が有意に高い残基群(’hotspot residues’: 以下、ホットスポット)を同定し、さらに、ホットスポットをタンパク質の立体構造および機能アノテーションと照合することで (下図左 Figure. 1参照)、タンパク質変異による癌化の機序解明を試みた。
入力データ
- TCGAとICGCのデータベース由来:130万種類の変異;10,000種類の腫瘍サンプル;22種類の組織;40種類の腫瘍型
データ解析
- インハウスのPerlスクリプトと独自に開発したR/Bioconductorパッケージ 'DominioEffect'により解析 (上図右 Figure EV1.参照)
- 160種類のタンパク質における180種類のホットスポットを同定;TCGAとICGC由来データの36%が、少なくとも1種類のホットスポットを帯びていた。
- 既知のドライバー遺伝子が54種類含まれていた(すなわち、106種類は既知のドライバー遺伝子と一致しなかった)。
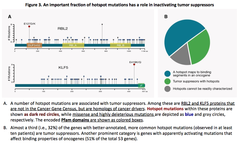
- ホットスポットを帯びたタンパク質は主として、酵素、ブロモドメインまたはKHドメインを帯びたタンパク質であった。また、多くが、腫瘍抑制因子を不活性化する調節因子であった(例:細胞周期を調節する網膜芽細胞腫様タンパク質p130 (RBL2)イタリック;クルッペル様因子5 (KLF5)イタリック (下図左 Figure 3 参照:))。
- PDB登録構造とホモロジーモデリング由来の3次元構造にマップにより、87種類のタンパク質のホットスポットが、他のタンパク質や核酸またはリガンドと結合する領域にマップされた(例:RXRA/PPARG/NCOA2ペプチド/レチノイン酸/DNA;CARM1二量体;CAND1/CUL1/RBX1 (下図右 Figure 4参照))。

- 1種類以上の腫瘍型の患者 (TCGAとICGC由来) の少なくとも3分の1以上で変異が見られるホットスポットと、主として由来組織に依存する腫瘍型 (crisp_bio注:Pan-Cancer Atlas報告前の腫瘍型)とのヒートマップから、同一遺伝子内の異なるホットスポットはクラスターを形成し、また、このクラスターと腫瘍型のクラスターが相関することが見えてくる(下図 Figure 5参照)

- crisp_bio関連記事: 2018/04/10「Pan-Cancer Atlas論文:癌ドライバー遺伝子と変異の網羅的同定と解析」; 2018/04/08「Tuba-seqとCRISPR-Cas9多重遺伝子編集により、腫瘍抑制因子変異の組合せが癌化に与える影響を定量化」; 2017/04/26「HotSpot3D: タンパク質3次元構造上での変異ホットスポットの同定と機能解析」


コメント